INTEGRIERTE CHROMATOGRAPHIE
Zwei oder drei Schritte. Ein Lauf. 2D/3D Integrated Batch.
Ihre Batch-Methode ist bereits Schritt eins. ChromaCraft™ ergänzt den nächsten — und orchestriert die mehrstufige Aufreinigung auf dem Contichrom® CUBE in einem einzigen integrierten Lauf, mit automatisiertem Transfer, In-line-Verdünnung und vollständiger Methodenkontrolle über alle Dimensionen hinweg.

Ein System. Zwei oder drei Aufreinigungsschritte.
Sobald Sie Ihre erste Batch-Methode auf dem Contichrom® CUBE ausführen, haben Sie die Grundlage für einen 2D-Aufreinigungsprozess geschaffen. Dieselbe Hardware, dieselben Säulen und dieselbe ChromIQ®-Software, mit der Ihr Protein-A-Capture durchgeführt wurde, können das Eluat direkt auf eine zweite Säule leiten – IEX-Polishing, HIC, Entsalzung –, ohne den Lauf zu unterbrechen.
Der CUBE übernimmt die Übergabe automatisch:
- In-line-Verdünnung zwischen den Schritten
- Kein Zwischentank
- Kein manuelles Eingreifen
- Keine separate Methodendatei pro Säule
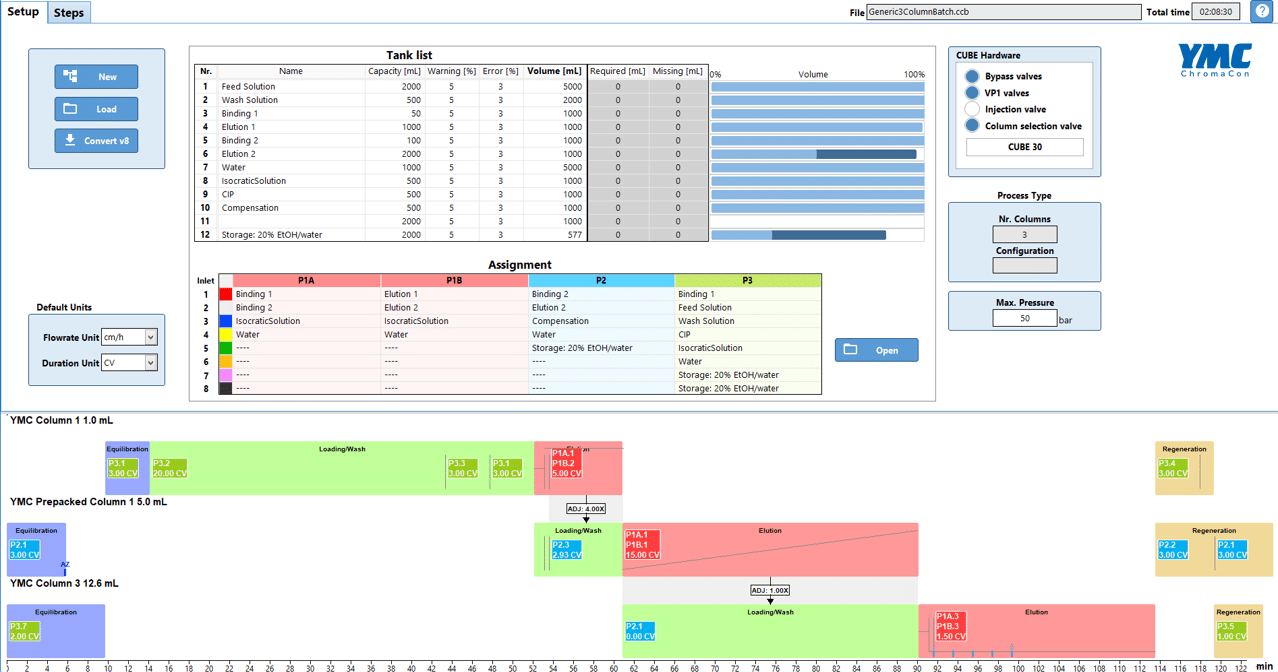
Das ist 2D-integrierte Batch-Chromatographie. Fügen Sie einen dritten Säulenschritt hinzu, wird daraus 3D. Die Twin-Column-Ventilarchitektur des CUBE unterstützt beides nativ, und ChromaCraft™ entwirft die komplette Methode im selben visuellen Gantt-Diagramm-Editor, den Sie bereits für Single-Column-Batch verwenden.
Das Ergebnis ist eine automatisierte, durchgängige Aufreinigungskette — von Capture über Polishing bis Desalting — abgeschlossen in einem einzigen unbeaufsichtigten Lauf. Sammeln Sie einen Produktpool oder fraktionieren Sie nach Bedarf. Die Zeit von der Beladung bis zur finalen gereinigten Fraktion sinkt von Tagen auf Stunden.

So funktioniert es
Das Ventilnetzwerk des CUBE verbindet den Auslass der ersten Säule direkt mit dem Einlass der zweiten. Wenn die UV-Kurve der Dimension 1 das Product Transfer Window erreicht, das Sie in ChromaCraft™ festgelegt haben, leitet ChromIQ® das Eluat in Dimension 2 um und wendet eine In-line-Verdünnung im von Ihnen angegebenen Verhältnis an.
Das Transferfenster kann auf zwei Arten ausgelöst werden:
- Absoluter mAU-Schwellenwert — wird bei einem festen UV-Wert ausgelöst (Peak-Front-Marker)
- Relativer Prozentsatz des Peak-Maximums — wird bei einem Bruchteil der beobachteten Peakhöhe ausgelöst (Peak-Tail-Marker)
Die Pumpen passen sich automatisch an. Keine manuellen Schritte zwischen den Etappen.
Dimension 2 führt anschließend ihre eigene Äquilibrier-, Bind-, Wasch- und Elutionssequenz aus, gesteuert durch die für diese Säule definierten Methodenparameter. Beide Schritte laufen innerhalb derselben ChromIQ®-Methode.
Für 3D-Methoden fügen Sie mit dem Column Selection Valve Kit eine dritte Säulenposition hinzu — eine vollständige Capture → Polishing → Desalting-Kette in einem automatisierten Lauf.

Unterstützte Schrittkombinationen auf dem Contichrom® CUBE:
| Format | Schritt 1 | Schritt 2 | Schritt 3 | Erforderliches Zubehör |
|---|---|---|---|---|
| 2D | Isokratisch (z. B. Protein A, IMAC) | Isokratisch (z. B. SEC, Desalting) | — | Column Bypass Valve Kit |
| 2D | Isokratisch (z. B. Protein A) | Gradient (z. B. CIEX, AEX, HIC) | — | Column Bypass Valve Kit |
| 2D | Gradient (z. B. RP) | Gradient (z. B. AIEX) | — | Column Bypass Valve Kit + Buffer Selection Valve Kit |
| 3D | Isokratisch | Gradient | Isokratisch (z. B. Desalting) | Column Bypass + Column Selection Valve Kits |
| 3D | Isokratisch | Gradient | Gradient | Column Bypass + Buffer Selection + Column Selection Valve Kits |
Ergebnisse analysieren: Das Evaluation Center
Beide Dimensionen eines 2D- oder 3D-Laufs werden im Evaluation Center in einem einzigen, kontinuierlichen Laufdatensatz erfasst. Die UV-Spur umfasst die komplette Methode — Sie sehen die Elution der Dimension 1, den Transferpunkt und das Chromatogramm der Dimension 2 (und Dimension 3) als eine einzige Zeitleiste.
- Peak-Integration — automatisch oder manuell, unabhängig auf das Elutionsprofil jeder Dimension angewendet
- Fraktionsanalyse — final gesammelte Fraktionen werden der vollständigen Laufspur zugeordnet; Reinheit und Ausbeute in einer Ansicht bewertet
- Laufvergleich — mehrere 2D/3D-Läufe überlagern, um die Reproduzierbarkeit sowohl des Transfer-Timings als auch des finalen Produktpeaks zu bestätigen
- PDF-Report-Export — vollständiger, strukturierter Bericht über alle Dimensionen hinweg, inklusive Transferparameter
- Excel-/CSV-Export — vollständige Signaldaten und Integrationsergebnisse über den gesamten mehrstufigen Lauf
Das ChromIQ®-Logbuch protokolliert jedes Systemereignis — einschließlich des Product-Transfer-Window-Triggers — in einem unveränderbaren Audit-Trail mit Datenintegritäts-Prüfsummen und mehrstufiger Benutzerrechteverwaltung.

Plattformvorteile auf einen Blick
| Vorteil | Was es in der Praxis bedeutet |
|---|---|
| Keine Puffertanks zwischen den Schritten | Eluat wird automatisch von Säule zu Säule übertragen — kein Zwischenbehälter, keine manuelle Handhabung, keine Wartezeit |
| In-line-Verdünnung integriert | Ionenstärke- oder pH-Anpassung zwischen den Dimensionen erfolgt über das Pumpennetzwerk — kein separater Verdünnungsschritt |
| Ein einziger Produktpool | Fraktionssammlung erfolgt einmal, am Ende der finalen Dimension — nicht nach jedem Schritt |
| Reduzierter QC-Aufwand | Ein Laufdatensatz, ein Chromatogramm, ein Report — statt drei pro Downstream-Schritt |
| Gleiche Hardware wie im Batch | Keine zusätzliche Systemanschaffung — 2D/3D-Läufe auf dem CUBE, den Sie bereits haben, mit Zubehör-Ventilkits |
| Direkter Scale-up-Pfad | 2D-Methoden lassen sich direkt auf die Contichrom® PILOT 300X- und TWIN-Systeme übertragen |
Anwendungen
| Molekülklasse | Typische 2D/3D-Konfiguration |
|---|---|
| Monoklonale Antikörper (mAbs) | 2D: Protein-A-Capture → CIEX-Polishing; 3D: Protein A → CIEX → Desalting — vollständige Downstream-Kette, ein Lauf |
| ADCs | 2D: Protein-A-Capture → HIC (DAR-Fraktionierung); oder HIC → IEX-Polishing |
| Rekombinante Proteine / Hormone | 2D: His-Tag-IMAC → IEX-Polishing; 3D: Protein L → IEX → SEC |
| Peptide | 2D: RP-Polishing (Dim 1) → AIEX-Polishing (Dim 2) — orthogonales Gradient-Gradient; oder RP → Desalting |
| Oligonukleotide | 2D: AEX-Gradient → RP-Polishing; orthogonale Selektivität, ein automatisierter Lauf |
| AAV / Gentherapie | 2D: Affinitäts-Capture → IEX-Polishing |
| mRNA / LNP | 2D: Affinität → IEX im passenden Maßstab |
| Nutraceuticals / Small Molecules | 2D: RP → Mixed-Mode- oder Normalphasen-Polishing |
Ein System. Zwei oder drei Aufreinigungsschritte.